Oligonucléotide
Définition
L'oligonucléotide est un polymère composé généralement de 15 à 30 nucléotides, où chaque unité est constituée d'une nucléobase, d'un sucre et d'un groupe phosphate. Un nucléotide est considéré comme l'élément constitutif de base des polymères d'acide nucléique (par exemple l'ADN et l'ARN).
Une partie monomère de l'oligonucléotide morpholino :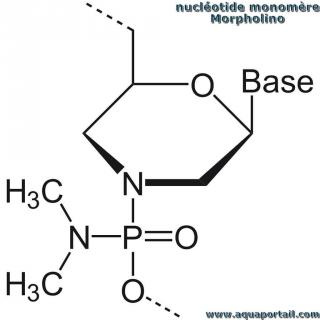
Un morpholino est un oligonucléotide utilisé dans la technologie antisens pour induire l'inactivation de gènes. Ils sont également connus sous le nom de PMO (phosphorodiamidate morpholino oligo).
Explications
Un oligonucléotide est une courte séquence à base d'ADN ou d'ARN, de cinquante paires de bases ou moins. Les oligonucléotides sont des oligomères construits à partir de quelques nucléotides. Chaque composant d'unité monomère est composé d'une nucléobase, d'un fragment pentose et d'un groupe phosphate. La séquence de nucléotides comprend entre 15 et 30 unités de nucléotides pour de nombreuses applications.
Ils ont des fonctions différentes : ils sont utilisés comme amorces dans les réactions d'amplification, comme sondes d'hybridation et dans des blocs spécifiques d'ARN messager. Ils se lient facilement à des oligonucléotides complémentaires ou à des acides nucléiques, formant un duplex. Ainsi, ils sont utilisés pour détecter la présence d'acides nucléiques.
Les aptamères sont des oligonucléotides qui peuvent se lier à une molécule spécifique via leur structure 3D.
Synthèse d'oligonucléotides
Un oligonucléotide est une molécule complexe formée à son tour de plusieurs nucléotides, chacun d'eux étant composé d'une base azotée, d'un hydrate de carbone et d'un groupe phosphate. La synthèse des oligonucléotides repose sur une série de réactions dans lesquelles les différents centres réactifs de la molécule sont cycliquement protégés et déprotégés :
- Protecteur hydroxyle en 2': Tert-butyl diméthylsilyle (TBDMS).
- Protecteur du phosphate libre : B-cyanoéthyle.
- Protecteur des hétérocycles de base : différents groupes amides.
Les oligonucléotides sont synthétisés par la méthode phosphoramidite sur phase solide (synthèse en phase solide). Durant la synthèse recombinante, il est possible d'incorporer des modifications telles que les marqueurs de fluorescence.
Oligonucléotides antisens
Les oligonucléotides antisens (ASO), sont de courtes molécules d'ADN simple brin (et dans certains cas d'ARN) complémentaires d'une séquence donnée. La séquence à laquelle ils se lient est généralement une molécule d'ARNm qui, liée par une ASO spécifique, ne peut plus être traduite. Les mécanismes par lesquels un bloc de traduction intervient sont essentiellement deux :
- Activation d'ARN, tels que les ARN H ou ARN L, qui dégradent l'ARNm avant sa traduction sur le ribosome;
- le blocage mécanique du ribosome, par la formation d'un double brin sur l'ARNm en cours de traduction.
Les oligonucléotides antisens ont de nombreuses applications cliniques : le premier médicament ASO à entrer sur le marché (1996) était le Vitraven, un antiviral approuvé par la FDA et l'EMEA exclusivement pour le traitement de la rétinite à cytomégalovirus chez les sujets immunodéprimés réfractaires au traitement classique.
Les oligonucléotides antisens sont des brins simples d'ADN ou d'ARN qui sont complémentaires d'une séquence choisie. Dans le cas des ARN antisens, ils empêchent la traduction de la protéine de certains brins d'ARN messagers en se liant à ceux-ci. L'ADN antisens peut être utilisé pour cibler un ARN complémentaire spécifique (codant ou non codant). Si une liaison existe, cet hybride ADN/ARN peut être dégradé par l'enzyme RNase H. L'utilisation d'oligonucléotides morpholino-antisens pour l'inactivation de gènes chez les vertébrés, qui est maintenant une technique standard en biologie du développement et utilisée pour étudier la modification de l'expression et de la fonction des gènes, a été développée par Janet Heasman sur des grenouilles Xenopus.
Applications en thérapie génique
Les oligonucléotides sont utilisés en thérapie génique comme stratégie pour l'extinction des gènes. Des oligonucléotides de 12 à 20 paires de bases complémentaires des ARN messagers des gènes que nous souhaitons réduire au silence sont utilisés.
Dans la cellule, l'oligonucléotide se lie à son ARN messager cible et bloque sa traduction. En d'autres termes, le ribosome traduira l'ARN messager jusqu'à ce que l'oligonucléotide soit trouvé et que le processus s'arrête. De plus, le fait que la RNase H reconnaisse l'hybride oligo-ARN et le dégrade constitue un autre avantage de cette technique. Il est important de concevoir l'oligonucléotide près du début de la traduction ou de s'assurer que le produit éventuellement obtenu n'a pas de fonction biologique, afin que l'extinction de gène soit efficace.
Les oligonucléotides idéaux pour la thérapie génique doivent présenter les caractéristiques suivantes :
- Ils doivent former des complexes stables avec le matériel génétique.
- Ils doivent être spécifiques à la cible.
- Ils doivent avoir une stabilité élevée et une demi-vie plus longue que d'habitude pour résister aux nucléases.
- Ils devraient pouvoir passer sans problèmes à travers les membranes cellulaires.
- Ils ne doivent pas s'accumuler dans les organes cellulaires ni dans les organites.
- Sa taille doit être comprise entre 18 et 20 paires de bases.
Les oligonucléotides peuvent être utilisés in vivo, mais ils ont une demi-vie très courte et une faible concentration. Précisément parce qu'il n'a pas d'effets durables, le principal problème des oligonucléotides en tant que thérapie génique est qu'ils nécessitent des doses successives.
Ils sont modifiés chimiquement pour avoir une demi-vie plus longue, soit dans l'oxygène des ponts de phosphate, soit dans les bases, soit dans le phosphate qui ne se trouve pas dans les ponts. Ils sont donc considérés comme un médicament, car ils ne modifient pas l'ADN et finissent par se dégrader.
Les applications possibles des oligonucléotides pourraient être trouvées dans les traitements antiviraux, antibactériens, antiparasitaires, anticancéreux ex vivo, dans le traitement des maladies de la peau, dans l'inhibition de l'inflammation, dans la suppression des oncogènes ou dans la suppression des gènes dominants.
Les puces à ADN sont construites en utilisant des oligonucléotides synthétiques fixés (haute densité) sur un support (tel que le nylon ou le verre). Actuellement, les microréseaux sont utilisés par exemple pour des études de polymorphisme et d'expression génique.
Oligonucléotides pour saut d'exon
Dans les mutations qui entraînent une fin anticipée de la traduction, les oligonucléotides seraient utilisés pour induire un traitement alternatif dans l'ARN messager mutant, sans inclure l'exon contenant la mutation. De cette manière, le codon d'arrêt prématuré ne serait pas lu par le ribosome et la protéine pourrait continuer à être traduite, le produit final serait alors le même que celui du gène normal, sans mutation.
Oligonucléotides catalytiques
Si une molécule d'EDTA-Fe se lie à l'oligonucléotide, cela entraîne la destruction active de l'ARN messager auquel elle se lie, ce qui permet de libérer l'oligonucléotide pour dégrader un autre ARN messager.
Triple hélice
Un oligonucléotide pourrait également se lier au double brin de l'ADN, donnant lieu à une structure connue sous le nom de triple hélice. S'il se lie à un gène particulier, il inhiberait sa transcription et, par conséquent, le ferait taire. Seulement deux oligonucléotides par cellule seraient nécessaires (un pour chaque chromosome de la paire), de sorte que le problème de la dose serait évité. Cette technique serait utile pour les mutations dominantes. Cependant, le super enroulement de l'ADN et son interaction avec les histones empêchent l'entrée de l'oligonucléotide dans le double brin.
Oligodésoxyribonucléotides
Les oligodésoxyribonucléotides (ODN) sont des oligonucléotides développés pour des applications cliniques dans de nombreuses maladies. S'agissant de molécules hautement spécifiques (parce qu'elles sont conçues pour correspondre à des séquences cibles spécifiques), elles présentent un intérêt considérable pour les industries pharmaceutique et biotechnologique, souhaitant identifier des médicaments spécifiques, efficaces et ayant peu d'effets secondaires, comme promettent d'être les ODN.
En réalité, les ODN sont des médicaments très puissants. Malheureusement, leur utilisation est fortement limitée par leur stabilité physico-chimique réduite, mais surtout par leur capacité modeste à imprégner les membranes cellulaires pour atteindre les acides nucléiques cibles. Pour surmonter ce problème, plusieurs modifications ont été apportées à la structure chimique native de ces molécules, avec des résultats contradictoires.
Il existe d'autres types d'oligodésoxyribonucléotides :
- Anti-gène : gènes spécifiques à une cible, où ils forment des triples hélices correspondant aux caractères homopyrimidine, bloquant leur réplication.
- Leurre ADN et leurre ARN : il s'agit de fragments d'oligonucléotides capables de se lier et de bloquer les facteurs de transcription et de traduction, respectivement.
- ribozymes : ARN cible. Ce sont des séquences d'ARN capables de se replier et d'avoir une activité catalytique, telles que la dégradation d'un ARNm complémentaire.
- Aptamères : ce sont des protéines ODN ciblant des protéines qui se lient et se désactivent avec une sélectivité élevée.
Synonymes, antonymes
Voir tous les synonymes pour "oligonucléotide".3 synonymes (sens proche) de "oligonucléotide" :
0 antonyme (sens contraire).
Les mots ou les expressions apparentés à OLIGONUCLÉOTIDE sont des termes qui sont directement liés les uns aux autres par leur signification, générale ou spécifique.
Le mot OLIGONUCLEOTIDE est dans la page 1 des mots en O du lexique du dictionnaire.
Mots en O à proximité
oligoélément oligohalin oligolécithe oligomère oligomérisation oligonucléotideoligopeptide oligophage oligophagie oligophotique oligopotence
En rapport avec "oligonucléotide"
Le Northern Blot est l'une des principales techniques d'analyse moléculaire, qui consiste à mesurer le niveau d'expression d'un gène...

Un dinucléotide est une combinaison chimique composée de deux nucléotides, chaque nucléotide étant formé d'un phosphate, d'un pentose...

Un dinucléotide CpG (site CpG) est une combinaison chimique de deux nucléotides, qui ont les nucléobases cytosine et guanine.

La flavine adénine dinucléotide (FAD) est un cofacteur capable de subir une action redox, présente dans plusieurs réactions...
